Nature Commun最新,Spectronaut软件针对pSILAC数据分析的具体操作逻辑
2025-07-02 16:06:37, omicsolution.com 上海易算生物科技有限公司

今天广泛使用的蛋白质组实验,往往只能捕捉细胞某一时刻的静态快照,但真实细胞中蛋白质却始终处在不停地合成与降解的流动过程中。如何精准捕捉这种动态变化?
脉冲稳定同位素标记(pulse-SILAC,pSILAC)能在特定时刻向细胞培养基中加入带有稳定同位素标记的氨基酸,让新合成的蛋白质具有“重”标记,而原有蛋白质保持“轻”标记,从而明确区分新旧蛋白质,测量蛋白质的动态周转。
pSILAC数据最突出的特点是每个时间点都同时包含两套肽段信号(即“轻”和“重”同位素信号)。不同于传统蛋白质组实验数据的单通道、静态特性,pSILAC数据随标记时间动态变化:
在标记初期,原有的“轻”肽段信号占据绝对优势,而新合成的“重”肽段信号微弱甚至缺失;随标记时间延长,“重”肽段逐渐成为主导信号,而“轻”肽段信号显著下降。
这种动态、不对称的双通道信号给数据分析带来了特殊挑战,需要在算法设计上特别优化。Spectronaut软件正是因为具备出色的双通道信号提取能力和精确定量优势,成为pSILAC数据分析中的主流选择。
近期,耶鲁大学医学院刘延盛教授团队在《Nature Communications》发表 A robust multiplex-DIA workflow profiles protein turnover regulations associated with cisplatin resistance and aneuploidy 的研究,详细阐述了基于Spectronaut的pSILAC数据分析流程。在附件中公开了软件具体参数与每一步的设置逻辑,提供了难得的实践经验。
我们特意将其整理,以便国内研究人员快速掌握这一经典分析策略,更精准地应用于自己的研究工作。

启动directDIA分析,选择质谱数据文件(支持.d或.raw格式)。

选择对应的蛋白序列数据库(FASTA文件)

同位素标记设置:在Labeling标签中明确指定标记类型,如Channel 1为无标记,Channel 2为Arg10、Lys8
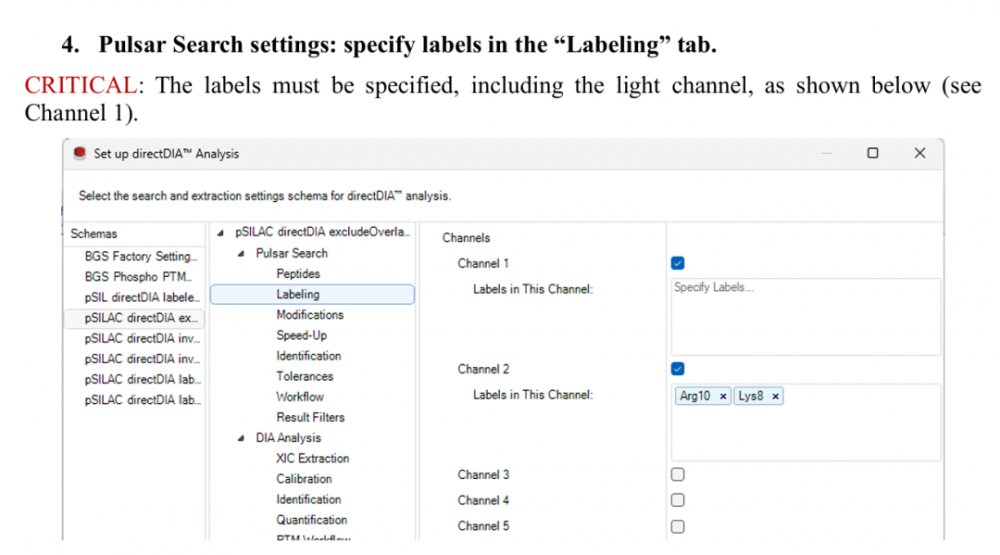
缺失通道生成(In-Silico Generate Missing Channels):在Workflow标签中启用此选项

碎片离子过滤(Fragment ion filtering):在Result Filters标签中选择Overlapping between Channels时,共享的碎片离子完全排除用于鉴定与定量;若未勾选则共享碎片仅在定量时排除(鉴定是保留的)。此选项对后续特定通道FDR过滤(如Min Q-value和Max Q-value)关键。

3.1 定量过滤(Quantification filtering)
可选“Group Q-value”(推荐默认)、“Min Q-value”、“Max Q-value”或“ChannelQ”。
“Group Q-value” 为跨通道综合评分;“Min Q-value” 至少一个通道需通过q < 0.01;“Max Q-value” 所有通道均需通过q < 0.01。
“Cross-run normalization” 使用所有通道之和推荐开启以稳定通道间差异。
“Exclude All Multi-Channel Interferences” 必须开启,以排除干扰离子(如pSILAC中的b离子)。
“Minimum Log2 intensity” 推荐设定值为3,用于排除极低的定量值。

3.2 工作流定义(Workflow)
在“Workflow”设置中选择“From Library Settings”以自动继承前一步设定(例如“Labeled” workflow)。

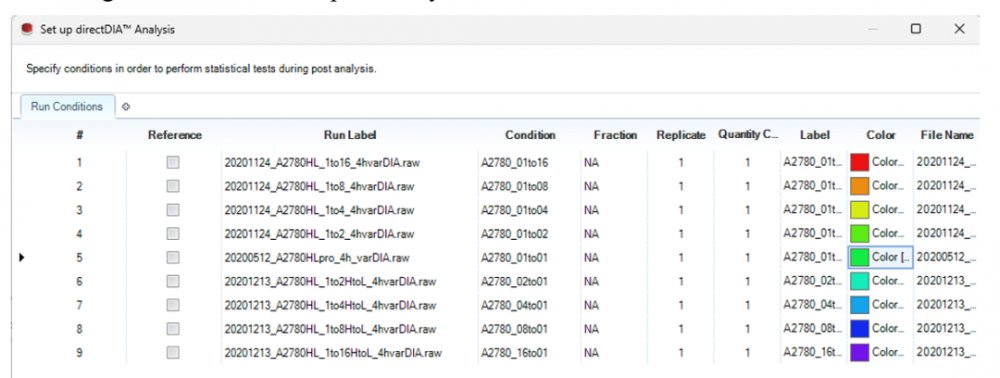
可为数据后续分析定义条件(Conditions)和颜色(Colors),便于结果可视化与后续分析。此设置可在分析后阶段修改。
选择好所有参数后启动分析。

分析完成后,Spectronaut提供以下多通道数据质控的可视化功能:
Scoring Weight per Channel Plot
显示每个通道在不同样品和时间点上的得分权重。
位置:Post Analysis → Scoring Histograms。

H/L Ratios Boxplot
显示每个样品和时间点的H/L比值分布,快速质控整体标记效率。
位置:Post Analysis → SILAC H/L Ratios。

H/L Cross Run Ratios Plot
对单个蛋白质的轻重通道强度绘制线性拟合,斜率即代表蛋白H/L比值。可进行过滤或手动挑选前体进行定制化分析。
位置:Analysis标签,选具体蛋白,在Across Runs选项卡内选择H/L Cross Run Ratios Plot。

Spectronaut分析完成后提供以下主要输出供后续工具(如KdeggeR)使用:
导出用于KdeggeR的数据:
要包含前体唯一ID列(EG. PrecursorId)与PG唯一ID列(PG. ProteinGroups);
要导出轻信号(EG. Channel1Quantity)与重信号(EG. Channel2Quantity)。
导出特定通道q-value以便自定义过滤:
EG.Qvalue(elution group整体的q值);EG.Channel1Qvalue 和 EG.Channel2Qvalue(单独通道的q值);EG.MinChannelQvalue 和 EG.MaxChannelQvalue(进一步通道过滤的q值)。
以上,我们梳理了Spectronaut在脉冲SILAC(pSILAC)数据分析每一步的具体操作逻辑。原文及其附件公开了详细的分析流程和软件参数设定,我们特此进行了中文整理与归纳,以方便国内研究人员更好地掌握和应用pSILAC技术。
如需了解更多细节或引用原始数据,请参考原始文献(见文末)。希望能够为大家解决pSILAC数据分析中的实际难题,更为各位的蛋白质组学研究增添新的助力与灵感。


04-22 谱临晟
荧飒光学践行企业社会责任,赋能光电人才高质量培养04-22 荧飒光学
报名通知丨英斯特朗塑料力学测试高阶培训研讨会04-22 英斯特朗
成都科林分析邀您共赴TFF·2026酒类风味分析与感官评价暨创新技术论坛,期待与您相遇!04-22
吉艾姆4月双展齐发 | 武汉科仪展+脂在浙里研讨会04-22
应用笔记 | 基于Flex自动化平台的多体液胞外囊泡分离及EV蛋白质组学分析流程04-21 肖伟弟 曾嘉明
CCMT2026开展即高能 | Equator-X™ 双模式测量仪引爆全场04-21
告别预测偏差!Percepta自建专属训练库,pKa预测更准更快04-21 ACDLabs 李丹
世界地球日,查看地球的【愿望清单】04-21
【前沿激荡,智汇北京】IGC 2026圆满落幕,益世科生物共绘细胞基因治疗新蓝图04-21
硬核方案护航核安全|衡昇质谱斩获核材料检测装备大奖04-21
会议预告 | 英盛生物邀您共赴2026第六届北京临床质谱论坛!04-21
Turbiscan在陶瓷3D打印粘结剂分散稳定性表征中的应用及关键意义04-21 大昌华嘉
GranuCharge (粉体静电分析仪)用于研究湿度对粉末表面性能的影响04-21 大昌华嘉
生物打印鼻软骨的理想材料:GelMA水凝胶的力学与细胞外基质平衡新探索04-21 大昌华嘉生命科学
Biolin Theta系列接触角测量 | 如何在表面表征应用中使用接触角:前进角04-21 大昌华嘉
大昌华嘉科学仪器荣获Novasina 2025年度“成长与创新先锋奖”!04-21 大昌华嘉
会议预告|华大吉比爱邀您共赴第六届北京临床质谱论坛04-21 华大吉比爱
叮咚!您有一份来自地球的“绿色盲盒”待拆封04-21 安捷伦科技
聚焦小核酸与多肽前沿分析:第一届创新药物研发与质量评价技术交流会在沪圆满举办04-21 安捷伦科技