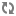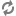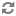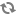400-6699-117转1000
咨询列表
上海欧易生物医学科技有限公司
您好,欢迎您查看分析测试百科网,请问有什么帮助您的?



| 参考报价: | 面议 | 型号: | 简化基因组甲基化测序MethylRAD-Seq |
| 品牌: | 欧易生物 | 产地: | 上海 |
| 关注度: | 1199 | 信息完整度: | |
| 样本: | 典型用户: | 暂无 |
400-6699-117转1000
简化基因组甲基化测序MethylRAD-Seq
Methyl RAD技术(Wang et al., Open Biol., 2015)使用了甲基化修饰依赖性内切酶,如FspEI、MspJI、LpnPI、AspBHI等,此类内切酶会识别DNA上发生甲基化的胞嘧啶,在识别位置的下游隔一定距离切割双链。若DNA双链具有中心对称甲基化状态,则可以切割产生一个固定长度的双链DNA片段。对酶切产生的标签建库测序,即可进行甲基化位点的定性和相对定量分析。
欧易特色
文库构建简便快速,不经过片段大小选择,保证了实验的重复性
具有较强的灵活性,标签密度可控
标签长度一致,PCR扩增效率一致,测序深度均一
具有单碱基分辨率,可以做到甲基化位点的定性和相对定量分析
甲基化位点检测的假阳性率能够控制在0.50%以内(WGBS假阳性率在0.28%-0.50%)
提供标准和高级生物信息分析,可根据客户需求提供个性化数据分析
所需的样本DNA起始量较低
有参无参物种均可,既可用于未知甲基化位点的开发,也可用于不同样本间的甲基化位点的差异研究
推荐测序模式
● Hiseq X-Ten,PE150 ● 30 M reads/1 G基因组大小
案例展示
案例一 腭融合过程 EMT 机制调控研究
研究背景
腭突上皮细胞发生上皮-间质转化(EMT)是腭融合的关键环节,但是分子水平的调控机制,尤其是胚胎腭发育过程中的增强子甲基化的调控研究,仍不清楚。
研究内容
欧易生物携手汕头大学医学院第二附属医院,采用 Methyl RAD 技术对 6 个小鼠胚胎上鄂组织(实验组为全反式视黄酸处理;对照组为等量的玉米油处理)进行全基因组甲基化研究,通过筛选差异甲基化位点(CCGG 和 CCWGG)、GO 和 KEGG 富集分析,发现腭融合过程调控 EMT 的 3 个基因的增强子甲基化水平发生变化,可作为唇裂治疗的新表观遗传标记。

研究结果
1. 6 个小鼠胚胎上颚组织共获得 800M clean reads,其中 325M reads 具有酶切位点,234M reads 能比对到参考基因组。检出的差异甲基化位点 CCGG 和 CCWGG 位点分别为 17299 个和 2363 个(p < 0.05, log2FC >1),CCGG 位点平均深度不低于 29X,CCWGG 位点平均深度不低于 8X。
2. 聚类分析结果表明,差异甲基化位点在实验组的甲基化水平高于对照组的甲基化水平,另外,实验组和对照组的甲基化模式不同,存在明显的个体内和个体间甲基化差异。
3. 相比于 DNA 元件中的其他区域,大多数甲基化位点位于内含子和基因间区。
4. 筛选与腭部融合有关、并调控 EMT 的基因,并检测这些基因增强子的甲基化变化,结果 HDAC4、PDGFR 和 TCF7L2 的差异甲基化位点 CCWGG 位于内含子的非 CpG 岛。其中,HDAC4 增强子的差异甲基化位点发生了高甲基化,而 PDGFR 和 TCF7L2 增强子的差异甲基化位点发生了低甲基化,可作为腭融合治疗的靶标。
参考文献
Shu X, Shu S, Cheng H, et al. Genome-Wide DNA Methylation Analysis During Palatal Fusion Reveals the Potential Mechanism of Enhancer Methylation Regulating Epithelial Mesenchyme Transformation. DNA Cell Biol 2018; 37(6): 560-573. (IF: 2.236).
常见问题
1. Methyl RAD 技术中使用的是什么类型的酶?
以其中一种内切酶 FspEI 为例,其识别序列为 5’-CC-3’,且第二个胞嘧啶需发生甲基化,在此胞嘧啶所在链的右侧第 12 个碱基处、反向链右侧第 16 个碱基处进行切割,此时若反向链中心对称位置上存在同样的识别位点,则可切割产生 Methyl RAD标签,用于建库测序。
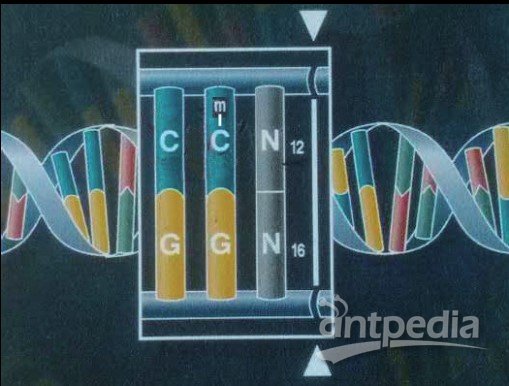
内切酶 FspEI 的识别及酶切位点
2. Methyl RAD检测到的甲基化位点数量如何?
Methyl RAD技术文章(Wang et al., Open Biol., 2015)中有Methyl RAD 和WGBS在拟南芥中检测到的CCGG和CCWGG两种甲基化位点的数量对比,从中可以看出二者的检出数量吻合度非常高。
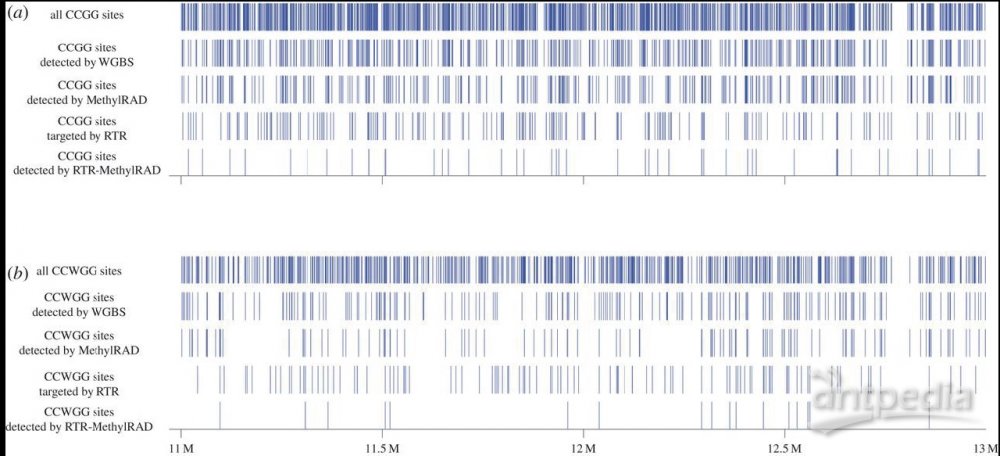
Methyl RAD、W GBS检测到的甲基化位点数量对比
(a、b图中的三行分别对应:基因组上预测出来的、WGBS检测到的、MethylRAD检测到的CCGG/CCWGG位点)
3. 如何调整标签密度?
Methyl RAD技术既可以增加标签密度,也可以降低标签密度。增大密度:可同时使用两种或两种以上的内切酶进行建库测序;降低密度:酶切后产生的片段为粘性末端,并且粘性末端的碱基是随机的。因此,在对酶切片段连接接头的过程中,可通过选择性接头特异地选择部分标签进行建库,以达到降低密度的目的。
参考文献
Wang S, Lv J, Zhang L, et al. MethylRAD: a simple and scalable method for genome-wide DNA methylation profiling using methylat ion-dependent restriction enzymes. Open Biol. 5, (2015). (IF: 4.822)
甲基化测序MethylRAD-Seq信息由上海欧易生物医学科技有限公司 为您提供,如您想了解更多关于甲基化测序MethylRAD-Seq报价、型号、参数等信息,欢迎来电或留言咨询。
注:该产品未在中华人民共和国食品药品监督管理部门申请医疗器械注册和备案,不可用于临床诊断或治疗等相关用途